БИОИНФОРМАТИЧЕСКИЙ АНАЛИЗ ЭВОЛЮЦИИ СИМБИОТИЧЕСКИХ ГЕНОВ КЛУБЕНЬКОВЫХ БАКТЕРИЙ СОИ НА ОСНОВЕ МУЛЬТИЛОКУСНОГО АНАЛИЗА ПОСЛЕДОВАТЕЛЬНОСТЕЙ
БИОИНФОРМАТИЧЕСКИЙ АНАЛИЗ ЭВОЛЮЦИИ СИМБИОТИЧЕСКИХ ГЕНОВ КЛУБЕНЬКОВЫХ БАКТЕРИЙ СОИ НА ОСНОВЕ МУЛЬТИЛОКУСНОГО АНАЛИЗА ПОСЛЕДОВАТЕЛЬНОСТЕЙ
Аннотация
В работе представлен биоинформатический анализ эволюции симбиотических генов клубеньковых бактерий сои (Glycine max L.) на основе мультилокусного анализа последовательностей (MLSA). Исследование выполнено на штаммах ризобий родов Bradyrhizobium и Rhizobium, выделенных из ризосферы сои в условиях Белгородской области. Для хромосомных маркеров (16S рРНК, rpoB, ITS) и симбиотических генов (nodC, nodD, nifH) проведены выравнивание последовательностей, расчёт показателей нуклеотидного разнообразия и реконструкция филогенетических деревьев. Показано, что симбиотические гены характеризуются существенно более высоким уровнем нуклеотидного полиморфизма по сравнению с хромосомными маркерами. Филогенетический анализ выявил устойчивую кластеризацию штаммов по хромосомным генам и повышенную вариабельность симбиотических детерминант, что указывает на их особую роль в адаптации микросимбионтов к растению-хозяину. Полученные результаты подтверждают эффективность MLSA-подхода для биоинформатического изучения эволюции симбиотических признаков ризобий сои.
1. Введение
Симбиотическая фиксация атмосферного азота бобовыми растениями является одним из ключевых биологических процессов, обеспечивающих устойчивость агроэкосистем и снижение зависимости от минеральных удобрений
, . Соя (Glycine max L.) формирует специализированный симбиоз с клубеньковыми бактериями, преимущественно относящимися к родам Bradyrhizobium и Rhizobium, геномы которых содержат гены, ответственные за нодуляцию и фиксацию азота . Традиционно для таксономической идентификации ризобий используется анализ гена 16S рРНК, однако многочисленные исследования показали его ограниченную разрешающую способность на видовом и внутривидовом уровнях . В отличие от него, белок-кодирующие хромосомные гены, такие как rpoB, а также межгенные регионы, демонстрируют более высокий уровень изменчивости и позволяют более точно разграничивать близкородственные таксоны .Особый интерес в последние годы вызывает изучение симбиотических генов (nod, nif), поскольку именно они определяют эффективность взаимодействия бактерии с растением-хозяином. Эти гены часто локализованы на симбиотических плазмидах или островках генома и подвержены горизонтальному переносу, что приводит к несоответствию между эволюцией хромосомного генома и симбиотических признаков
, , .С точки зрения биоинформатики это формирует важную научную задачу — сравнительный анализ эволюционных траекторий хромосомных и симбиотических генов. Мультилокусный анализ последовательностей (MLSA) позволяет интегрировать данные по маркерам различной степени консервативности и выявлять различия в уровне нуклеотидной изменчивости, отражающие как таксономические, так и адаптивные процессы. Применение MLSA-подхода открывает возможности для более глубокого понимания эволюции симбиотических признаков клубеньковых бактерий и оценки их роли в формировании эффективного симбиоза с соей
, .Целью настоящей работы являлся биоинформатический анализ эволюции симбиотических генов клубеньковых бактерий сои на основе мультилокусного анализа хромосомных и симбиотических маркеров.
2. Методы и принципы исследования
2.1. Биологический материал
Объектом исследования служили штаммы клубеньковых бактерий, выделенные из корневых клубеньков сои (Glycine max L.), выращенной на опытных участках Белгородского ГАУ. Чистые культуры получали на среде Виноградского и использовали для последующего молекулярно-генетического анализа.
2.2. Получение и обработка нуклеотидных последовательностей
Из полученных штаммов были амплифицированы и секвенированы фрагменты хромосомных генов 16S рРНК, rpoB, межгенного региона ITS (16S–23S рРНК), а также симбиотических генов nodC, nodD и nifH. Продукты ПЦР анализировали методом электрофореза в агарозном геле (рис. 1).
Электроферограмма продуктов амплификации генов 16S рРНК, rpoB, nodC:
M – маркеры молекулярной массы; дорожки 1-8 – амплифицированные образцы штаммов Bradyrhizobium sp. из клубеньков сои
2.3. Биоинформатический анализ
Редактирование и формирование консенсусных нуклеотидных последовательностей выполняли в программе BioEdit v7.2.5. Множественное выравнивание последовательностей проводили с использованием алгоритма ClustalW в программной среде MEGA X. Показатели нуклеотидного разнообразия (Pi) и количество полиморфных сайтов (S) рассчитывали с помощью программы DnaSP v5.10. Филогенетические деревья реконструировали методом neighbor-joining с использованием модели эволюционных расстояний Kimura 2-parameter и bootstrap-анализа (1000 реплик).
3. Основные результаты
3.1. Нуклеотидное разнообразие хромосомных и симбиотических маркеров
Хромосомные маркеры характеризовались низким уровнем нуклеотидной изменчивости. Ген 16S рРНК демонстрировал минимальные значения Pi, что отражает его высокую консервативность. Ген rpoB обладал более высоким уровнем полиморфизма и обеспечивал лучшую дифференциацию штаммов.
Симбиотические гены (nodC, nodD, nifH) отличались существенно более высоким нуклеотидным разнообразием (табл. 1), что указывает на интенсивные эволюционные процессы и возможную адаптацию к растению-хозяину.
Таблица 1 - Нуклеотидное разнообразие маркеров ризобий-симбионтов сои
Род бактерий | Маркер | Длина, п.о. | Pi | S | Характеристика |
Rhizobium | 16S рРНК | 1317 | 0,0123 | 120 | Консервативный |
Rhizobium | rpoB | 934 | 0,0629 | 312 | Дифференцирующий |
Rhizobium | nodC | 804 | 0,1356 | 364 | Высокополиморфный |
Bradyrhizobium | 16S рРНК | 1444 | 0,0051 | 48 | Консервативный |
Bradyrhizobium | rpoB | 940 | 0,0377 | 131 | Среднеполиморфный |
Bradyrhizobium | nodC | 780 | 0,0382 | 287 | Симбиотический |
3.2. Филогенетический анализ
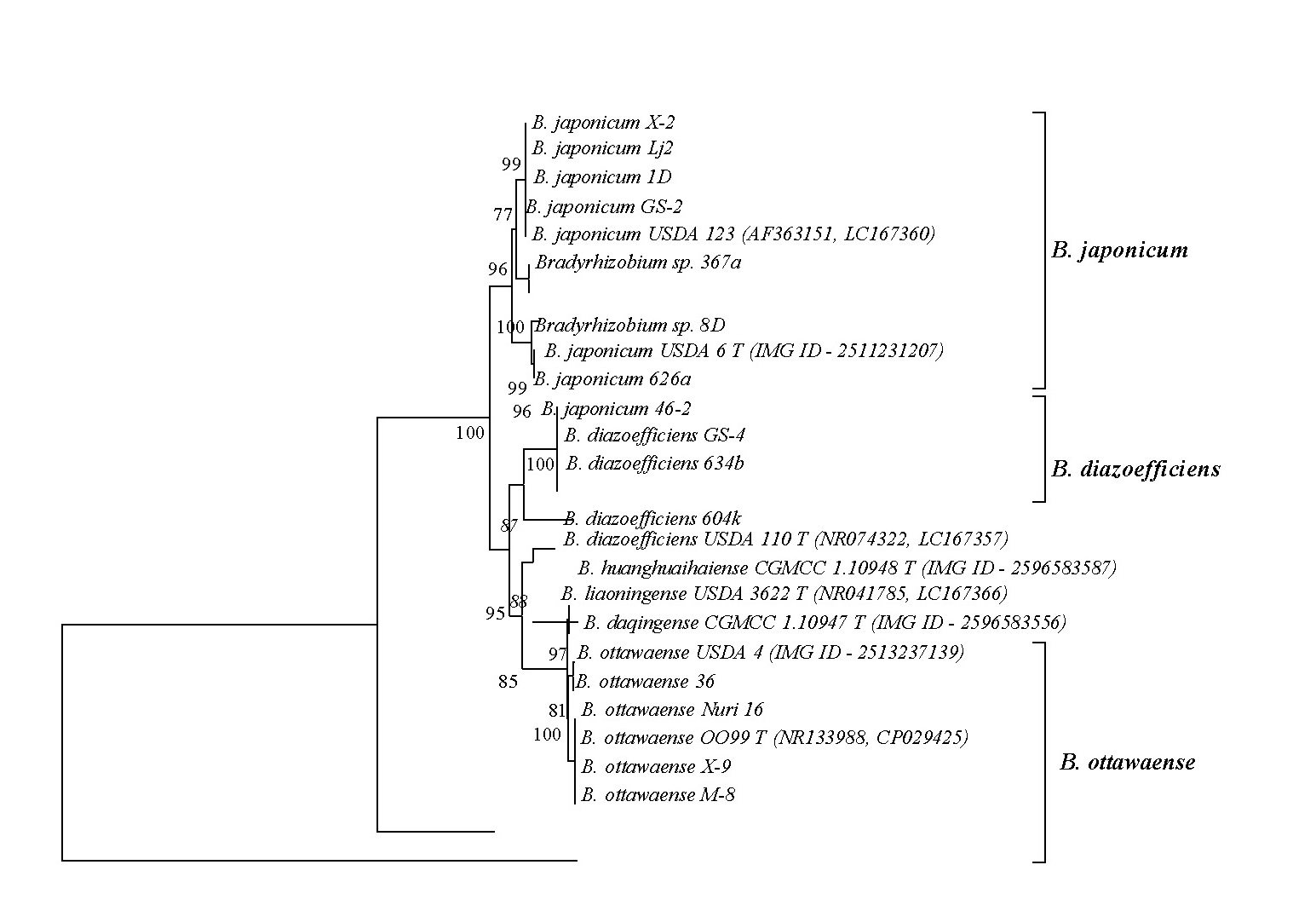
Филогенетическое дерево клубеньковых бактерий сои, построенное на основе мультилокусного анализа хромосомных генов
4. Обсуждение
Выбор генетических маркеров для изучения клубеньковых бактерий является критически важным аспектом исследований. Традиционно используемый ген 16S рРНК, несмотря на свою универсальность, часто оказывается недостаточно информативным для видовой дифференциации из-за своей высокой консервативности. В то же время белок-кодирующие гены, такие как rpoB и gyrB, а также межгенный регион ITS, демонстрируют более высокий уровень полиморфизма, что делает их предпочтительными для филогенетических исследований.
Симбиотические гены, такие как nodC и nifH, играют ключевую роль в формировании клубеньков и фиксации азота, но их использование для таксономии ограничено из-за частого горизонтального переноса между различными штаммами. Тем не менее, эти гены представляют большой интерес для изучения эволюции симбиоза и адаптации бактерий к конкретным растениям-хозяевам.
Практическое значение данного исследования заключается в возможности использования полученных данных для подбора эффективных штаммов-инокулянтов, способных повысить урожайность сои. Кроме того, понимание генетического разнообразия клубеньковых бактерий может способствовать разработке новых биотехнологических подходов в сельском хозяйстве.
5. Заключение
В ходе исследования проведён биоинформатический мультилокусный анализ эволюции симбиотических генов клубеньковых бактерий сои. Показано, что симбиотические гены (nodC, nodD, nifH) характеризуются существенно более высоким уровнем нуклеотидного полиморфизма по сравнению с хромосомными маркерами, что отражает их важную роль в адаптации микросимбионтов к растению-хозяину.
Филогенетический анализ подтвердил эффективность MLSA-подхода для разграничения близкородственных видов рода Bradyrhizobium и выявления внутривидового разнообразия. Полученные результаты подчёркивают значимость биоинформатических методов для изучения эволюции симбиотических признаков и могут быть использованы при отборе перспективных штаммов-инокулянтов для агробиотехнологических применений.
